細胞培養解析装置CS-1 - アプリケーション
細胞コンフルエンシーの推定
深層学習により,iPS細胞の領域を認識し,コンフルエンシーを計測できます!
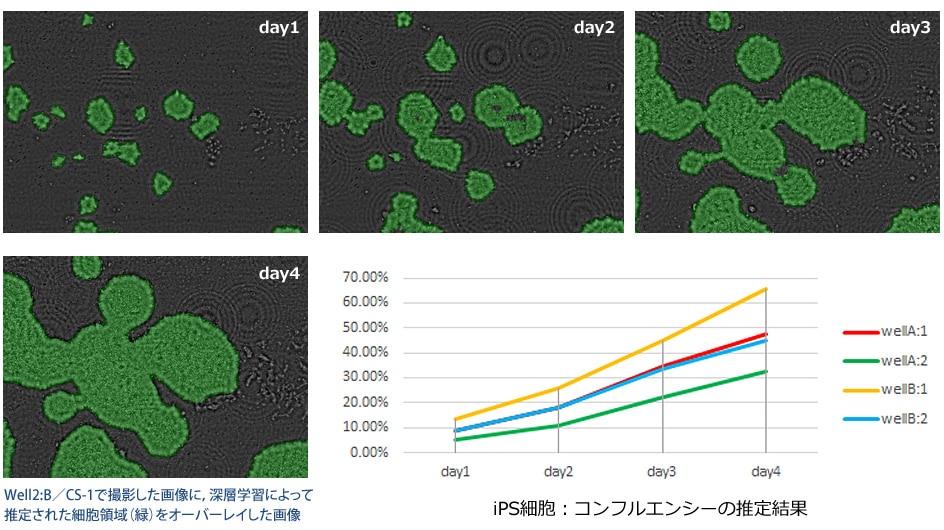
|
実施例 |
: |
4日間培養したiPS細胞をCS-1で1日1回撮影し,その画像中に占めるiPS細胞コロニーの領域を深層学習によって推定した。推定された面積からコンフルエンシー変化を定量した。 |
|
推定対象 |
: |
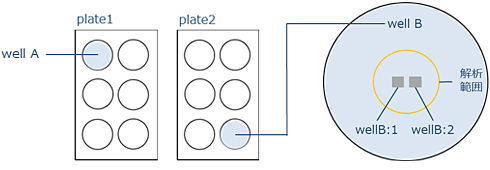
iPS細胞(1231A3株)の内,未分化状態のコロニー。2プレートの対象で,それぞれ1wellから中央2視野分を対象とした。 |
|
教師データ作成 |
: |
評価対象とは異なるウェルの画像を対象とし,目視にて細胞領域を指定し,細胞領域と背景を識別する画像データを作成した。 |
|
評価方法 |
: |
教師データ作成方法と同様の手法で評価用データの細胞領域と背景を識別し,その結果と深層学習による推論結果と比較しAccuracyとIoUを評価した。 |
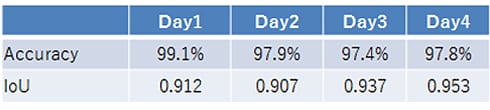
深層学習による推定の評価結果:
4日間の培養において,各培養日ごとに二つのプレートから各2視野分,合計4視野のコンフルエンシ―を推定しました。4視野のAccuracyは97%程度、IoUは0.9程度となる推定結果を得られました。
Appendix:評価指標AccuracyとIoUについて
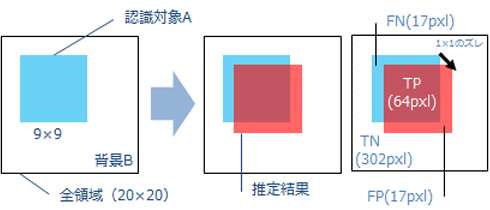
20×20pixelの領域にある9×9pixelの物体を検出する時,左図のように上下方向,左右方向で1pixelずつずれて推定された場合
Accuracy : (TP+TN)/ALL = 91.5%
IoU :TP/(TP+FN+FP) = 0.653
TP:True Positive / Aと予想して正解もA
FP:False Positive / Aと予想したが正解はB
TN:True Negative / Bと予想して正解もB
FN:False Negative / Bと予想したが正解はA
他の細胞への適用例
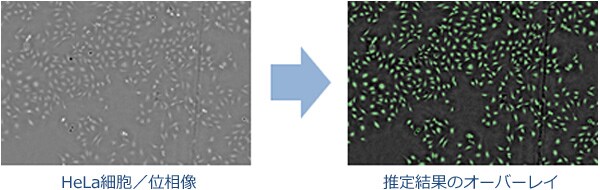
HeLa細胞のような非コロニー性の細胞領域も推定することができます。
CS-1では強度情報に依存せず安定した画質で撮影できるため,深層学習を始めとする機械学習の推定に有意な画像を得られます。
光学厚みによる分化細胞と未分化細胞の識別
CultureScannerは,光学厚みという定量情報が表示可能です。そこで,この新たな定量情報となる光学厚みを用いて,iPS細胞の未分化維持コロニーと未分化逸脱細胞が識別可能であるか検討しました。

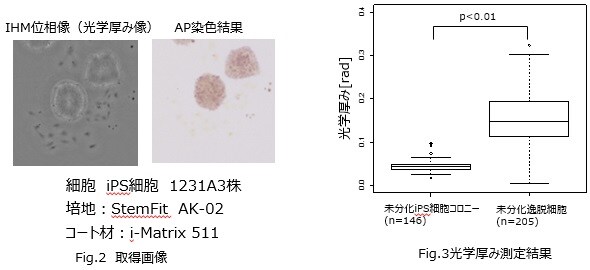
まず,未分化iPS細胞コロニー(①)と未分化逸脱細胞(②)をIHM方式でスキャンした後,未分化性を,AP染色により確認しました。 次に,IHM位相像から,①と②の光学厚みを測定しました(Fig.1,2)。①と②の光学厚みを比較したところ,有意な差が認められました(Fig.3)。
さらに,iPS細胞由来神経細胞の光学厚みを測定しました。分化誘導開始3日後までの細胞と,未分化iPS細胞コロニーの光学厚みを比較したところ,有意な差が認められました。
以上より,光学厚みは細胞を識別するための定量情報として,研究用途はもちろん,新たな工程管理指標としても活用できる可能性が示唆されました。


